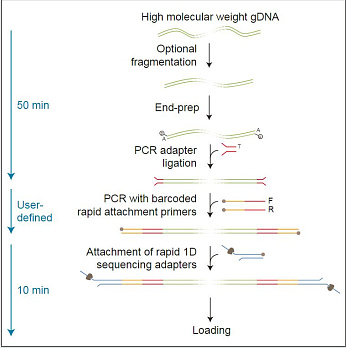
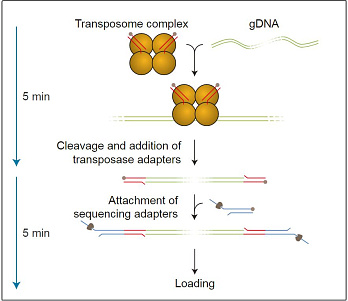
Набор предназначен для быстрого и простого получения сиквенсной библиотеки, включающей до 12 различных образцов ДНК, в тех случаях, когда количество ДНК
ограничено. С помощью набора
Rapid PCR Barcoding Kit можно:
- объединять несколько образцов ДНК в одну библиотеку;
- свести время пробоподготовки к минимуму;
- работать с небольшим исходным количеством ДНК;
- работать с загрязнённой ДНК.
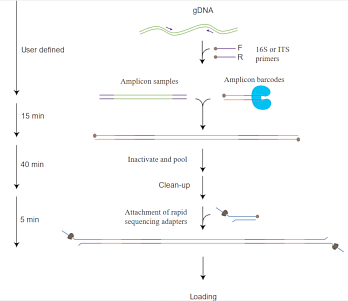
Объединение нескольких образцов, или мультиплексирование, возможно благодаря бар-кодированию разных ДНК. Это удобно в тех случаях, когда требуемый выход данных при секвенировании одного образца намного меньше максимального выхода, получаемого с одной проточной ячейки. В состав набора входит 12 бар-кодов, таким образом, в одну библиотеку можно загрузить до 12 образцов ДНК. Это позволяет снизить стоимость секвенирования одного образца почти в 10 раз.
Особенности набора:
|
время пробоподготовки
|
от 15 минут + ПЦР
|
|
требуемое количество ДНК
|
1-5 нг геномной ДНК
|
|
необходимость ПЦР
|
Да
|
|
фрагментация ДНК
|
транспозазная
|
|
длина рида
|
около 2 килобаз
|
|
производительность
|
1-2 гигабазы за 6 часов, 4-8 гигабаз за 48 часов
|
|
совместимые протоколы
|
Rapid PCR Barcoding Sequencing*
|
|
количество библиотек
|
6
|
* Полные протоколы доступны на сайте
www.nanoporetech.com для зарегистрированных пользователей-участников Nanopore Community.
Набор предназначен для исследований, требующих простой пробоподготовки и быстрого результата, но не максимальной производительности секвенирования.
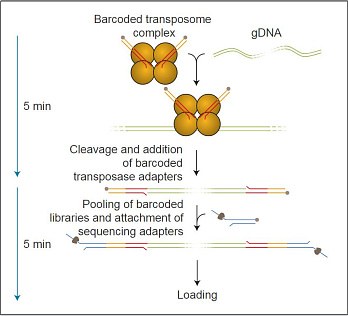
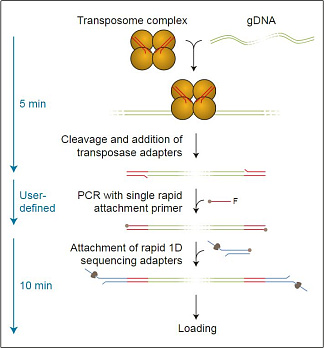
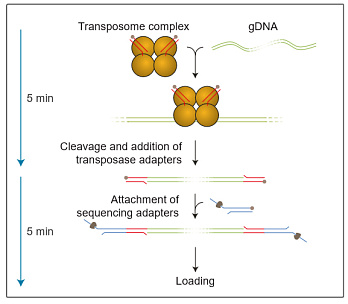
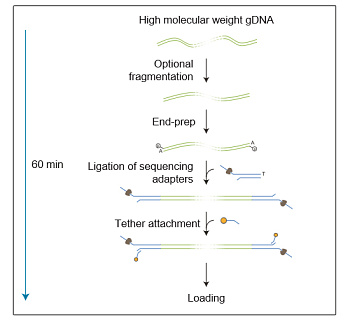
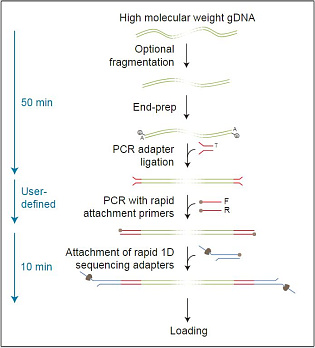
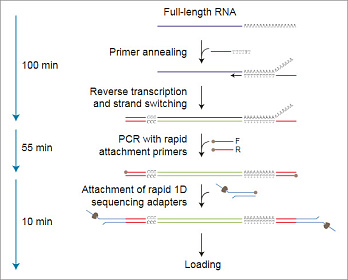
Пробоподготовка заключается в расщеплении ДНК транспозазой и присоединении к фрагментам олигонуклеотидов, содержащих сайты связывания ПЦР-праймеров. Затем каждый образец ДНК амплифицируется с помощью баркодированных праймеров. Баркодированные ампликоны объединяются, и к ним присоединяются сиквенсные адаптеры.
Длина ампликонов в среднем составляет около 2 килобаз и не зависит от длины исходной ДНК. Это связано в большей степени с особенностями пробоподготовки, а не с процессивностью Taq-полимеразы.
Поэтому для пользователей, работающих с малым исходным количеством геномной ДНК и желающих получить риды максимальной длины, рекомендуется набор Ligation Sequencing Kit и протокол Low input genomic DNA with PCR.
Набор позволяет работать с ДНК, содержащей примеси, которые снижают эффективность получения библиотеки. Это происходит благодаря стадии ПЦР. Но необходимо учитывать, что амплификация разных фрагментов может идти с разной эффективностью.
Если исходное количество ДНК менее 1 пг, рекомендуется полногеномная амплификация.
Сортировка ридов в соответствии с баркодами производится с помощью программных инструментов, доступных в рамках платформы EPI2ME.
В состав Rapid PCR Barcoding Kit также входит набор Flow Cell Priming Kit для загрузки библиотеки в поточную ячейку.
Условия хранения: -20 °С.
Дополнительные расходные материалы и реактивы:
- магнитные частицы Agencourt AMPure XP (Beckman Coulter);
- 1,5 мл пробирки типа Эппендорф с низкой адгезивностью DNA LoBind (Eppendorf 0030108051);
- 0,2 мл тонкостенные пробирки для ПЦР (Thermo FS AB0620);
- вода, не содержащая нуклеаз (Thermo FS R0581);
- мастер-микс для ПЦР LongAmp Taq 2X (New England Biolabs M0287);
- свежеприготовленный 70% этанол;
- буферный раствор Tрис-HCl 10 мМ рН 8.0 с 50 мМ NaCl.
Дополнительное оборудование:
- настольная микроцентрифуга (например, Eppendorf 5452000018);
- вортекс (например, Biosan BS-010203-AAG);
- магнитный штатив (Диаэм 3336);
- ротационный перемешиватель (например, Elmi RM1L);
- амплификатор;
- набор автоматических пипеток переменного объёма — от 0,5 до 10 мкл (например, Eppendorf 3120000020), от 2 до 20 мкл (например, Eppendorf 3120000038), от 10 до 100 мкл (например, Eppendorf 3120000046), от 20 до 200 мкл (например, Eppendorf 3120000054) и от 100 до 1000 мкл (например, Eppendorf 3120000062);
- наконечники с фильтром к автоматическим пипеткам;
- таймер (например, TR118OS).
Опционально:
- флуориметр Qubit (Thermo FS Q33227) или аналогичный;
- система для фрагментного анализа (например, Qsep 100);
- наноспектрофотометр (например, NanoDrop 2000C).